Met DNA-analyses zijn in diverse watertypen diatomeeën (kiezelwieren) geïdentificeerd. Een indexwaarde gebaseerd op DNA hoeft niet af te wijken van de met microscopisch onderzoek bepaalde waarde mét aantalsschattingen per soort.
Download hier de pdf van dit artikel
Geschreven door Michiel Hootsmans (KWR Water Research Institute), Kevin Beentjes (Naturalis Biodiversity Center), Berry van der Hoorn (Naturalis Biodiversity Center, hogeschool InHolland Delft) en Jako van der Wal (AQUON)
Diatomeeën (kiezelwieren) zijn belangrijke indicatororganismen. Ze reageren snel op veranderingen in hun milieu en van veel soorten zijn milieu-indicatiewaarden bekend [1]. Ze geven een beeld van milieucondities op een locatie over een periode van weken tot maanden (zie bijvoorbeeld [2], [3]). In 21 van de 27 EU-landen vormen diatomeeën onderdeel van een Kaderrichtlijn Water (KRW)-kwaliteitsindex voor stromende wateren. In negen EU-landen worden ze voor stilstaande wateren toegepast [4].
Vaak is de gebruikte maatlat gebaseerd op de Indice de Polluosensitivité Spécifique (IPS), die ook onderdeel is van de Nederlandse KRW-maatlat [5]. De determinatie van diatomeeën vereist hooggekwalificeerde kennis en is tamelijk kostbaar en tijdrovend. Diatomeeën zijn daarom in Nederland wel opgenomen in de KRW-beoordeling van stromende wateren, maar niet van stilstaande wateren. Daar is als alternatief gekozen voor waterplanten en het optreden van algenbloei. Voor stromende wateren is dat niet mogelijk.
De ontwikkeling van op DNA gebaseerde identificatiemethoden kan het gebruik van diatomeeën als indicatoren voor waterkwaliteit nieuw leven inblazen. Door lagere kosten per DNA-analyse kunnen meer monsters in ruimte en tijd worden genomen en kan de ecologische kennis over diatomeeën gemakkelijker en breder worden ingezet. Het beleid rondom de KRW focust op de grotere wateren (zoals rivieren, kanalen en meren van meer dan 50 ha).
DNA-technieken om diatomeeën te analyseren lenen zich ook uitstekend om ecologische effectbepaling toe te passen op de vele wat kleinere wateren die ons land rijk is. Zo ontstaan nieuwe kansrijke mogelijkheden voor monitoring, diagnose en beoordeling voor waterbeheerders en watergebruikers, nationaal en internationaal.
In 2020 is het onderzoeksproject DNA Diatom Biosensor gestart [6]. De hoop is om met DNA van diatomeeën een nieuwe biosensortechniek te realiseren, in samenwerking met een breed palet aan eindgebruikers (Stowa, de waterschappen Fryslân, Hollands Noorderkwartier, Rijnland, Delfland, Hollandse Delta, Schieland en de Krimpenerwaard, Stichtse Rijnlanden, Brabantse Delta, De Dommel en Limburg), marktpartijen (de laboratoria AQUON en Waterproef, en BaseClear) en de onderzoeksinstellingen Naturalis Biodiversity Center en KWR Water Research Institute.
In dit artikel worden de resultaten besproken van een eerste vergelijking tussen DNA-analyses en traditionele identificaties, gebaseerd op uiterlijke (morfologische) kenmerken. De onderzoeksvragen waar een antwoord op gezocht wordt, zijn:
● In hoeverre verschillen de op DNA gebaseerde soortenlijsten van de traditionele, morfologisch bepaalde, soortenlijsten van de onderzochte locaties?
● Wat is het effect van deze mogelijke verschillen op de waarde van de internationaal veel gebruikte diatomeeën-waterkwaliteitsindex IPS?
● In hoeverre wijken resultaten van oppervlaktewatermonsters af van substraatmonsters (materiaal afkomstig van stengels en takken)?
Methoden
Locaties
In maart 2021 zijn zes locaties bemonsterd die redelijk representatief zijn voor enkele Nederlandse wateren (zie ook afbeelding 1a en 1b): de Dieze (een sterk gekanaliseerde stroom), de Beeksche Waterloop (een behoorlijk stromende sloot), het ven Nieuw Karregat, de langzaam stromende Groote Wetering, een kleine poel bij de Groote Wetering en de Teeffelense Wetering.
Bemonstering
Op elke locatie werden meerdere rietstengels (of vergelijkbare objecten) verzameld in een oplossing van 96 procent ethanol, en werden watermonsters gefiltreerd en geconserveerd. Bij de Dieze konden alleen diatomeeën van de beschoeiing worden geschraapt. De waterbemonstering gebeurde met een filter met een poriegrootte van 5 micrometer. Dit water werd steekproefsgewijs bemonsterd in hetzelfde traject als de substraatbemonstering. Er werden geen monsters verzameld voor morfologische analyse. Behalve de poel bij de Groote Wetering zijn dit namelijk officiële KRW-monitoringslocaties, dus was er voor vijf van de zes locaties voldoende recente historische informatie beschikbaar.
Afbeelding 1a: Bemonsteringslocaties

Afbeelding 1b. De zes bemonsteringslocaties. (1) Dieze (1), (2) Beekse waterloop, (3) Nieuw Karregat , (4) Groote Wetering. (5) Poel bij Groote Wetering, (6) Teeffelense Wetering
DNA-extractie en -identificatie
In het lab werden voor elke locatie (indien mogelijk) drie typen monsters voorbereid voor DNA-extractie en verdere verwerking volgens [7]:
1. Het DNA-filter dat al op locatie was geconserveerd (hierna ‘eDNA-monsters’ genoemd)
2. Na een halve minuut hard schudden van de pot ethanol met daarin de stengels (of materiaal van de beschoeiing bij de Dieze) werd de suspensie met diatomeeën gebruikt voor de DNA-extractie (hierna ‘ethanolmonsters’ genoemd).
3. Na het schudden werd met een scalpel het oppervlak langs de gehele lengte van drie stengels afgeschraapt. Dit werd in ethanol gebruikt voor de DNA-extractie (hierna ‘schraapmonsters’ genoemd).
Met de DNA-extractie worden typerende stukjes DNA van diatomeeën verkregen (de zogenoemde DNA-barcodes). Voor het op naam brengen hiervan werd een publiek beschikbare referentiedatabase gebruikt (zie [8]). Deze bevat barcodes van diatomeeën wereldwijd, en ongeveer een kwart van de soorten die gebruikt worden voor de Nederlandse KRW-maatlat is hierin vertegenwoordigd. Er werd een soortnaam aan toegekend als een barcode voor minstens 98 procent overeenkwam met een barcode in de database.
Voor de overige barcodes werd zo mogelijk nog een bijbehorende naam van het genus (groep van verwante soorten) of de familie (groep van verwante genera) bepaald. Een deel van de barcodes kon niet worden geïdentificeerd. Dit betreft deels waarschijnlijk soorten die niet in de referentie zijn opgenomen, maar ook bijvangst van andere soortgroepen (dus geen diatomeeën). Er is internationaal nog veel werk te verrichten aan het goed koppelen van correcte morfologische identificaties aan bijbehorende DNA-barcodes.
Resultaten
Vergelijking DNA en morfologie
Voor een vergelijking van de aangetroffen diversiteit aan diatomeeën tussen de verschillende methoden is gekeken naar het aantal genera (groepen van verwante soorten; zie afbeelding 2). In de drie situaties met schraapmonsters is het aantal genera hierin lager of gelijk aan die in de ethanol en eDNA-monsters. In orde van grootte verschillen de aantallen met de vier methoden niet heel veel van elkaar.
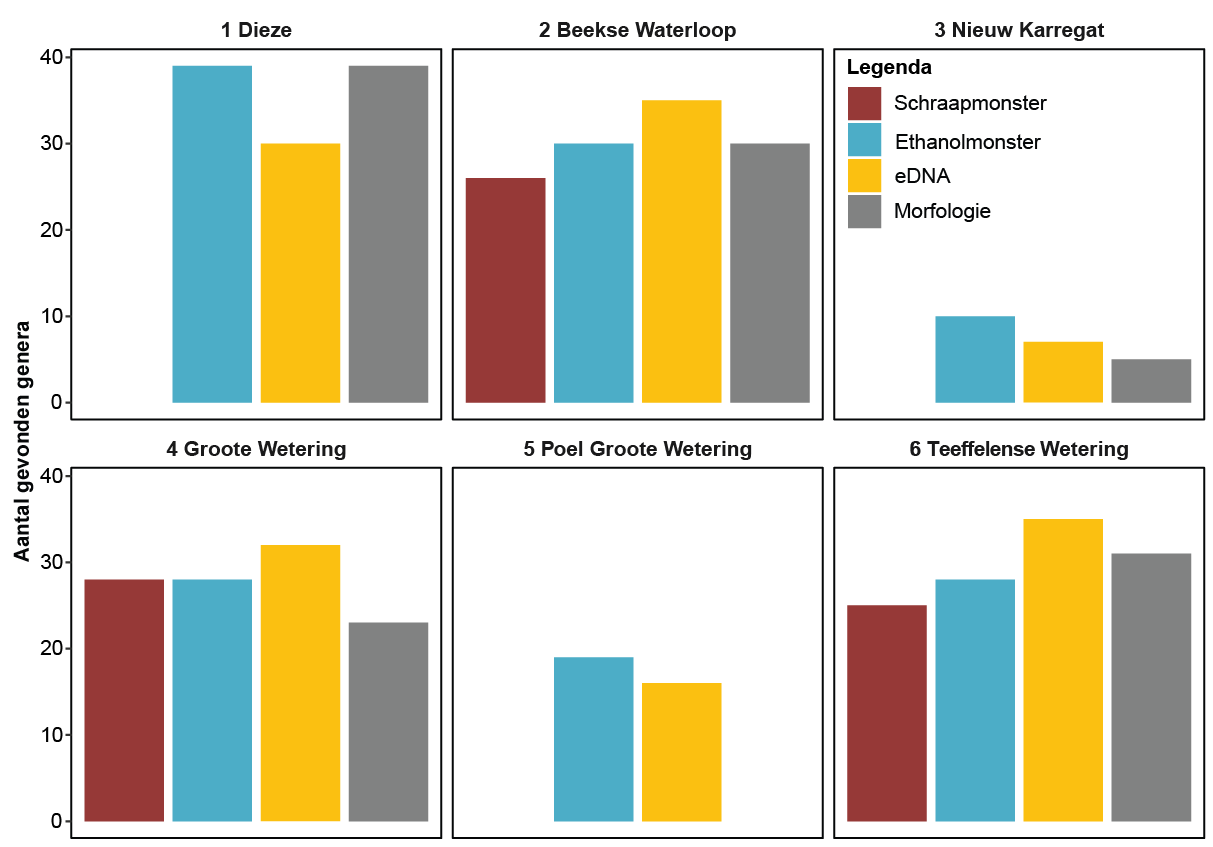
Afbeelding 2. Aantal gevonden genera voor de zes locaties op grond van de verschillende DNA-methoden (schraap, ethanol en eDNA) en op grond van beschikbare historische morfologische data (morfologie)
Bij de morfologische data gaat het echter om de resultaten van meerdere bemonsteringen in meerdere jaren. De morfologische dataset is dus vele malen groter dan de op DNA gebaseerde dataset. In afbeelding 3 is voor de drie locaties met vier datasets met zogenoemde Venndiagrammen de overlap tussen de vier methoden weergegeven. Zo’n twee derde van alle genera in de morfologische data is ook met de combinatie van ethanol- en schraapmonsters gevonden.
Het aantal uniek gevonden genera is het hoogste in de eDNA- en morfologische data. Dit is bij eDNA-monsters te verklaren door de aanwezigheid van planktonische (vrij in het water zwevende) genera. Bij de morfologische data komt dit vermoedelijk doordat deze een verzameling van meerdere historische monsters vormt en door genera die (nog) niet in de barcodereferentiedatabase zitten.
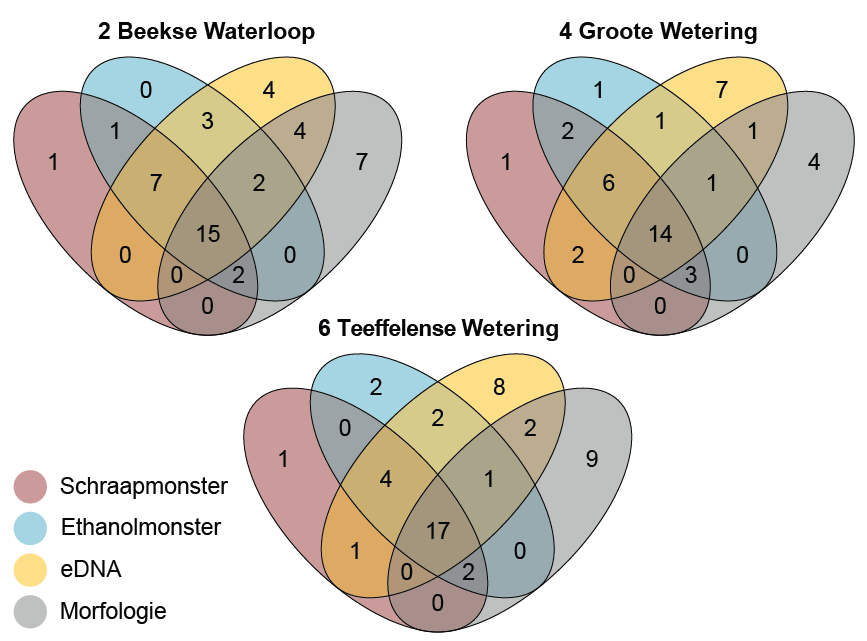
Afbeelding 3. Venndiagrammen van de overlap tussen genera in de verschillende methoden, voor de drie locaties waar data beschikbaar waren voor zowel morfologie als de drie verschillende DNA-methoden (schraap-, ethanol- en eDNA-monsters). NB: cirkelgrootte is geen indicatie voor aantallen genera
Vergelijking van IPS-waarden
Een belangrijke vraag is of de soortenlijsten op grond van de verschillende methoden tot een verschillende beoordeling van de waterkwaliteit leiden. Hiervoor zijn de IPS-scores berekend, als voorbeeld van een handig instrument om soortgerelateerde kwaliteitsinformatie samen te vatten tot één getal.
Voor de traditionele monitoring worden 200 diatomeeën per monster gedetermineerd en geteld en de aantallen per soort worden meegewogen in de IPS-score. Het bepalen van betrouwbare aantallen per soort is met DNA echter niet mogelijk. Er is daarom eerst gekeken wat de invloed was van het al of niet meenemen van de aantallen per soort op de IPS-score. In een eerder onderzoek naar zo’n effect op een KRW-index voor macrofauna (kleine waterdiertjes) bleken de aantallen individuen per soort slechts van beperkte invloed [9]. En ook voor de IPS lijkt dit zo te zijn, gezien de sterke correlatie tussen de waarden berekend mét en zonder aantallen (zie afbeelding 4).
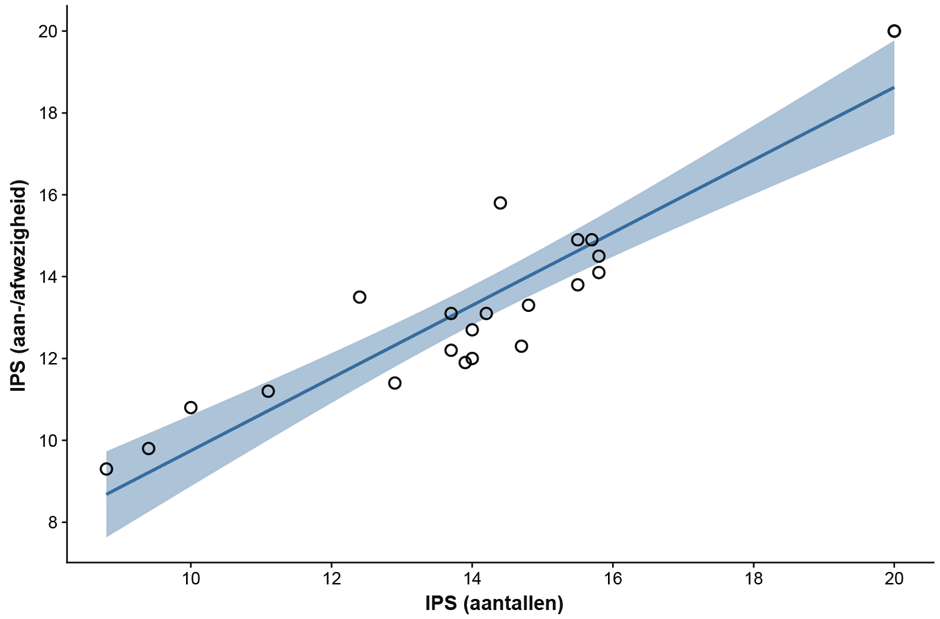
Afbeelding 4. IPS-waarden van de voor de zes onderzochte locaties beschikbare morfologische data, berekend mét (horizontaal: IPS-aantallen) en zónder de aantallen individuen per soort (verticaal: IPS-aan-/afwezigheid). Pearson-correlatie = 0.92 (p<0.001)
Voor de meeste locaties vallen de IPS-scores op basis van DNA-methoden binnen de spreiding die bestaat in de IPS-waarden op basis van de morfologische data (afbeelding 5; voor locatie 5, de poel bij de Groote Weetering, bestaan geen historische data).
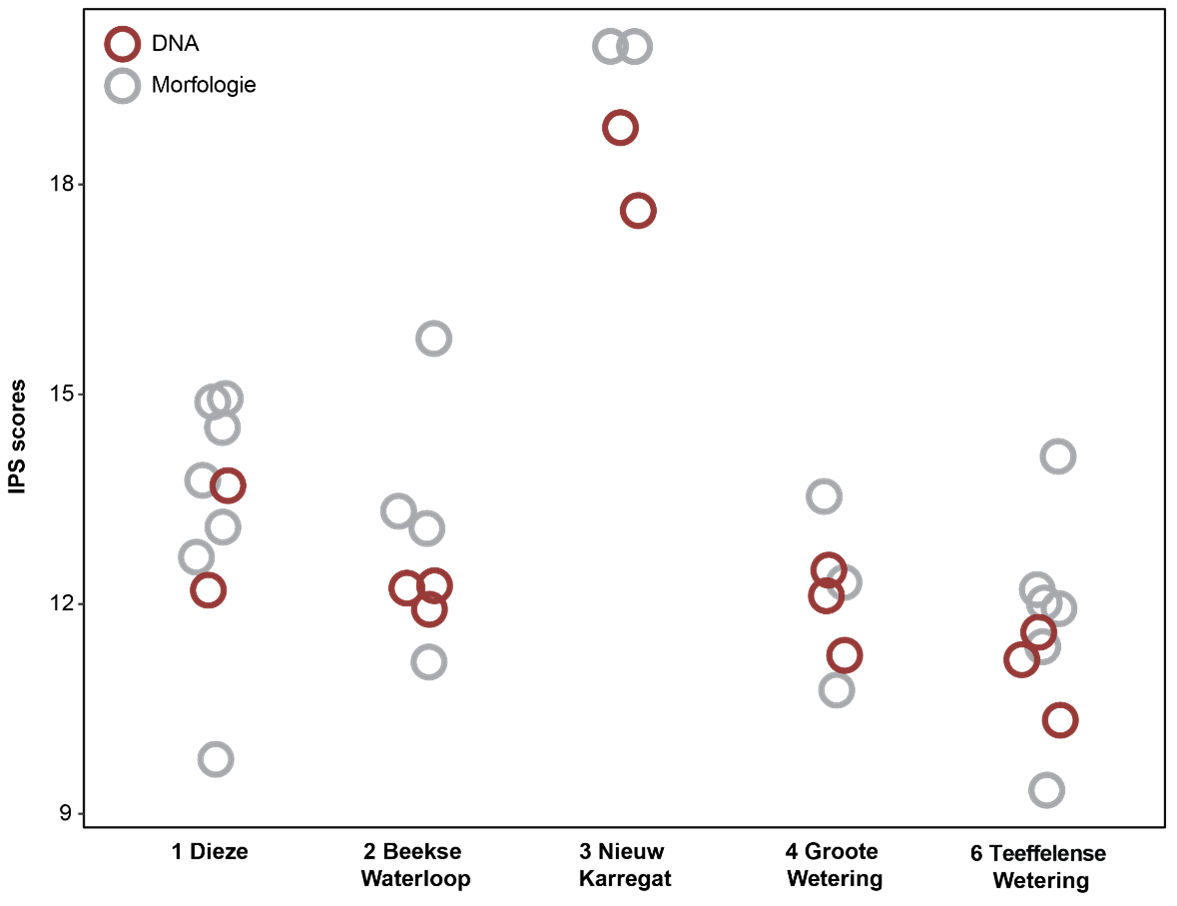
Afbeelding 5. IPS-scores gebaseerd op de soortenlijsten van zowel de historische morfologische analyses (grijs) als de drie DNA-gebaseerde methoden (rood) voor de vijf onderzochte locaties met morfologische data
Vergelijking DNA-methoden
In alle zes ethanol- en eDNA-monsters werden barcodes van diatomeeën aangetroffen. Ook voor drie van de vijf locaties met een schraapmonster was dit het geval. Alleen bij Nieuw Karregat en de poel bij de Groote Wetering hadden de schraapmonsters geen barcodes. Hier zijn mogelijk alle diatomeeën die op de stengels aanwezig waren al losgekomen bij het schudden van de pot met ethanol.
In afbeelding 6 is een overzicht te zien van de verdeling van de geïdentificeerde soorten over de tien meest voorkomende families van diatomeeën. In veel gevallen is de diversiteit redelijk vergelijkbaar tussen de drie typen DNA-monsters per locatie. De familie van de Stephanodiscaceae lijkt voornamelijk in de eDNA-monsters voor te komen. Deze familie bestaat uit vrij zwevende (planktonische) soorten. Deze worden daarom ook niet in grote aantallen verwacht in substraatmonsters.

Afbeelding 6. Verdeling van op soort te herleiden clusters van diatomeeën-barcodes (MOTU’s) over de tien meest voorkomende families, voor de zes locaties en de drie verschillende DNA-methoden (schraap-, ethanol- en eDNA-monsters)
Hoewel enkele soorten alleen werden gevonden in schraapmonsters, zijn de meeste unieke soorten alleen gevonden in ethanolmonsters. Dit suggereert dat veel diatomeeën al loslaten, al dan niet door te schudden, wanneer stengels in ethanol geplaatst worden.
Conclusies
De op DNA gebaseerde lijsten komen in belangrijke mate overeen met de traditionele, op morfologie gebaseerde lijsten. Ook de met DNA-resultaten berekende IPS-indexscores voor waterkwaliteit vallen meestal ruim binnen de bandbreedte van de op morfologie gebaseerde IPS-scores. De spreiding van morfologische IPS-scores is vaak groot, waarschijnlijk door jaarlijkse variatie in milieuomstandigheden. Morfologische IPS-waarden gebaseerd op de aan- en afwezigheid van soorten zijn goed gecorreleerd met de IPS berekend op basis van aantallen individuen per soort. Dat is belangrijk omdat deze aantallen per soort niet met DNA-analyses kunnen worden bepaald. Een op DNA gebaseerde IPS-waarde hoeft dus helemaal niet af te wijken van de IPS-waarde gebaseerd op morfologische data mét die aantalsinformatie.
Van de DNA-methoden lijkt schudden zonder schrapen het meest efficiënt. Dit levert bijna net zoveel diatomeeën op als mét schrapen. Vooralsnog blijven echter in het onderzoek beide handelingen toegepast worden, totdat ook uit een veel grotere dataset dezelfde conclusie kan worden getrokken. De diatomeeën die alleen in de schraapmonsters gevonden worden, kunnen immers van belang zijn voor de uiteindelijke interpretatie van de waterkwaliteit. Niet schrapen zou de laboratoriumwerkzaamheden echter wel sterk vereenvoudigen.
De diversiteit van de eDNA-monsters van het water is niet altijd representatief voor de op een locatie aanwezige diatomeeën gemeenschap op stengels en andere oppervlakken. Dat komt vanwege het aandeel vrij zwevende diatomeeën in het water en daarmee de gevoeligheid van eDNA-monsters voor effecten van aan- en afvoer van water. Niettemin komt de IPS-score van eDNA-monsters goed overeen met die van de substraatmonsters. Hoewel deze index niet is ontworpen voor eDNA-monsters lijken deze dus toch een goede indicatie (quick scan) te kunnen geven van de waterkwaliteit.
Vooruitblik
Momenteel worden in het onderzoeksproject DNA Diatom Biosensor de resultaten uitgewerkt van een grootschalige bemonstering in 2021 bij diverse betrokken waterschappen. Hiermee worden ecologische inzichten vergeleken die gebaseerd zijn op traditionele monitoring en op parallel daaraan verzamelde informatie uit op DNA gebaseerde soortenlijsten. Waar mogelijk wordt speciale aandacht besteed aan effecten van landbouwkundig- en waterbeheer gericht op vermindering van eutrofiëring. Daarnaast moet een overzicht van interessante reeksen historische data weer in herinnering brengen wat een waterbeheerder met diatomeeën kan zeggen over veranderingen in ecologische waterkwaliteit.
De DNA-benadering biedt ook mogelijkheden om barcodes van diatomeeën te gebruiken voor een waterkwaliteitsbepaling, zonder dat identificatie tot op soortniveau nodig is. Door deze onbekende diatomeeën te koppelen aan de ecologische kwaliteitsinformatie van de eveneens aanwezige bekende diatomeeën, kunnen ook die onbekende diatomeeën worden gebruikt als informatiebron wanneer ze elders worden aangetroffen. Zo kunnen nog veel meer diatomeeën bijdragen aan het verkrijgen van een goed beeld van de milieuomstandigheden onder water.
Financiering voor dit onderzoek kwam mede uit de Toeslag voor Topconsortia voor Kennis en Innovatie (TKI's) van het ministerie van Economische Zaken (Topsector Water).
REFERENTIES
1. Dam, H. van, Mertens, A., & Sinkeldam, J. (1994). ‘A coded checklist and ecological indicator values of freshwater diatoms from The Netherlands’. Neth. J. Aquat. Ecol. 28: 117-133.
2. Zuilichem, H. van, Peeters, E., & Wal, J. van der (2016). ‘Diatomeeën als indicator voor waterkwaliteit nabij rwzi’s?’ H2O-Online 9 december 2016.
3. Dam, H. van, & Mertens, A. (2020). ‘Kiezelwieren geven aan: zwavel en stikstof houden vennen in de greep’. Vakblad Natuur Bos & Landschap 170: 14-17.
4. Poikane, S., Kelly, M., & Cantonati, M. (2016). ‘Benthic algal assessment of ecological status in European lakes and rivers: challenges and opportunities’. Sci. Tot. Environ. 568: 603-613.
5. Molen, D.T. van der, Pot, R., Evers, C.H.M., Herpen, F.C.J. van, & Nieuwerburgh, L.L.J. van (2018). Referenties en maatlatten voor natuurlijke watertypen voor de Kaderrichtlijn Water 2021-2027. Stowa 2018-49, versie juni 2020.
6. https://www.tkiwatertechnologie.nl/projecten/dna-diatom-biosensor/ geraadpleegd op 8 september 2021.
7. Beentjes, K.K., Speksnijder. A.G.C.L., Schilthuizen, M., Hoogeveen, M., & Hoorn, B.B. van der (2019). ‘The effects of spatial and temporal replicate sampling on eDNA metabarcoding’. PeerJ 2019. doi: 10.7717/peerj.7335.
8. Rimet, F. et al. (2016). ‘R-Syst::diatom: An open-access and curated barcode database for diatoms and freshwater monitoring’. Database 2016:baw016. doi:
10.1093/database/baw016.
9. Beentjes, K.K., Speksnijder, A.G.C.L., Schilthuizen, M., Schaub, B.E.M., & Hoorn, B.B. van der (2018). ‘The influence of macroinvertebrate abundance on the assessment of freshwater quality in The Netherlands’. Metabarcoding and Metagenomics 2:e26744. doi: 10.3897/mbmg.2.26744.


















Bovendien nog een tweede prijs in Hoofddorp, de Winnaar van de Publieksprijs de Gerritshoeve / Kastan van Ontwerper Architectenbureau Gijs de Waal. (Winnaars Arie Keppler Prijs 2024 - Architectuur.nl) Ik heb vaak en veel moeten uitleggen waarom juist in deze ruimte vragende polder opnieuw een aanslag wordt gedaan op vruchtbare agrarische grond. *)
De aanleiding van mijn reactie is een fout in de oppervlakte maat van de Piekberging, 16 ha. moet 67 ha. zijn. Aansluitend heb ik nog een verzoek om met een link ook de informatie over de Piekberging zelf te ontsluiten: https://www.rijnland.net/actueel/nieuwsoverzicht/piekberging-haarlemmermeer-wint-arie-keppler-prijs-2024/
https://www.rijnland.net/wat-doet-rijnland/in-uw-buurt/piekberging-haarlemmermeer/
https://www.rijnland.net/wat-doet-rijnland/in-uw-buurt/piekberging-haarlemmermeer/veel-gestelde-vragen-piekberging-haarlemmermeer/ *)
Hoeveel kogels heeft men laten vallen (op verschillende plaatsen) om te concluderen dat de faalkans als gevolg van een impact (25 kg bal van 22 meter hoogte lijkt me inderdaad een aardige klap geven) op een voldoende laag niveau zit?